Identificação computacional de genes de microRNA
description
Transcript of Identificação computacional de genes de microRNA

Identificação computacional de genes de microRNA
Alexandre dos Santos CristinoBruno Augusto N. Travençolo
César Beltrán CastañónElza Helena Andrade Barbosa

Roteiro Introdução Caracterização biológica de miRNAs Predição computacional de miRNA
de Drosophila Validação experimental dos
candidatos à miRNA Conclusões

Introdução
rRNA
miRNA
miRNA
Interrupção

IntroduçãoRNA
mRNAncRNA
Non-coding RNA. RNA transcrito tem papel estrutural, funcional ou catalítico
rRNARibosomal RNA
Participa da síntese de proteínas
tRNATransfer RNAInterface entre
RNAm e aminoácidos
snRNASmall nuclear RNA
RNA que fazemparte do
spliceossomo
snoRNASmall nucleolar RNA
Encontrado no nucléolo e estaenvolvido na modificação
do RNAr
miRNAMicro RNA
Pequenos fragmentosde RNA que estão
envolvidos na regulaçãoda expressão gênica
OutrosRNAs maiores compondoa estrutura da cromatina
e relacionados ao “imprinting”
siRNASmall interfering RNAativa moléculas na
interferência por RNA
stRNASmall temporal RNA.RNA com função de
regulação do desenvolvimento biológico

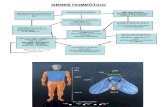
Caracterização biológica de miRNAsO que é um microRNA (miRNA)?
Nova classe de pequenos RNAs reguladores, “escondidos” no genoma (regiões intergênica e intrônica ou “DNA lixo”)
Estes miRNA de 22 nucleotídeos foram descobertos em estudos de regulação do desenvolvimento de C. elegans (lin-4 e let-7)
Alguns com expressão constitutiva, e outros com controle de expressão temporal- e tecido-específica

Caracterização biológica de miRNAs Inicialmente transcrito como um pré-miRNA
de 70-100 pb (stem loop, hairpin, double strand)
Pré-miRNA é processado pela Dicer (RNAase III)
Formação de miRNA “maduro” com 21-22 nt Atua negativamente na regulação pós-
transcricional pela formação de um duplex RNA, interrompendo a tradução de um RNAm pela região 3’-UTR
RNAi -> silenciamento gênico

Caracterização biológica de miRNAs
LoopmiRNA
Dicer (RNAase III)
UGAGGUAGUAGGUUGUAUAGU(miRNA)

Caracterização biológica de miRNAs
miRNA são altamente conservados em grupos filogenéticos afastados (insetos, peixe e humano)

Predição computacional de miRNA de Drosophila
Regras e parâmetros foram derivados a partir de 24 sequências de miRNA de Drosophila
O alinhamento global (VISTA) entre os genomas de espécies diferentes de Drosophila mostraram alta conservação nas 24 sequências de miRNA referência.

Predição computacional de miRNA de Drosophila
Alinhamento global D. melanogaster e D. pseudoobscura (VISTA plot)

Predição computacional de miRNA de Drosophila
O alto grau de conservação e a formação de stem-loop não são características exclusivas dos miRNAs
Portanto, foram necessários critérios adicionais, tais como determinar padrões de divergência dos nucleotídeos entre os 24 pares ortólogos

Predição computacional de miRNA de Drosophila
Resultado do Alinhamento
Conservação total (3/24)
diverge no loop (10/24)
Divergência no loop divergência em um
braço (10/24)
Divergência nos braços (0/24)
Divergência em um braço
(0/24)Divergência no braço
>> divergência no loop (1/24)

Predição computacional de miRNA de Drosophila Observações do conjunto referência (24
miRNA) indicam que os miRNAs são filogeneticamente conservados e a estrutura stem-loop demostra um padrão característico de divervêngia dos nucleotídeos.
miRseeker: pipeline desenvolvido para localizar candidatos a miRNA no genoma
Dividido em três partes: 1. Identificar regiões conservadas; 2. Identificar e avaliação da qualidade de stem-loops; 3. Avaliar padrões de divergência

Predição computacional de miRNA de Drosophila 1. Identificar regiões conservadas

Predição computacional de miRNA de Drosophila 1. Identificar regiões conservadas - AVID
D. Melanogaster
1287 contigs
D. Pseudoobscura
18000 contigs
AVID – Alinhamento Global
Eliminar os genes anotados, tais como: exons, transpossons, snRNA, snoRNA, tRNA, rRNA
Alinhamento total resultou em 51.3 de 90.2 MB de sequências intrônicas e intergênicas

Predição computacional de miRNA de Drosophila 1. Identificar regiões conservadas
Sem sobreposição e cruzamento
Prefere clean matches à repeated matches
Tamanhos maiores que a metade do maior match
Score baseado no tamanho e nos vizinhos

Predição computacional de miRNA de Drosophila 1. Identificar regiões conservadas
D. Melanogaster
1287 contigs
D. Pseudoobscura
18000 contigs
AVID – Alinhamento Global
Eliminar os genes anotados, tais como: exons, transpossons, snRNA, snoRNA, tRNA, rRNA
Alinhamento total resultou em 51.3 de 90.2 MB de sequências intrônicas e intergênicas

Predição computacional de miRNA de Drosophila 1. Identificar regiões conservadas
Determinar uma região candidata a miRNA Janela de 100 unidades (pares de nucleotídeos
alinhados ou gap) avança no alinhamento critério mínimo de conservação: 13% gaps e
15% mismatchs critério satisfeifo -> sequência Dm/Dp guardada em
arquivo multi-fasta -> janela avança 10 unidades 436.000 regiões conservadas em sequências
intrônicas e intergênica 118.000 super-regiões (agrupamento de regiões que
apresetaram sobreposição de 10 nt)

Predição computacional de miRNA de Drosophila2. Identificar e avaliar qualidade de stem-loops

Predição computacional de miRNA de Drosophila2. Identificar e avaliar qualidade de stem-loops
Análise de regiões conservadas com o algoritmo de dobramento de RNA (folding), mfold 3.1
miRNA pode estar localizado em qualquer uma das fitas (forward e reverse), o pode interferir na qualidade do hairpin predito
436.000x2 = 872.000 mfolds cutoff -> mínimo de 23 pares de bases e
energia livre de um braço G -23.0 kcal/mol

Predição computacional de miRNA de Drosophila2. Identificar e avaliar qualidade de stem-loops
Métricas para o helical score: Premia nucleotídeos pareados em +1 Penaliza cada loop simétricos de um nucleotídeo
em –1 Penaliza cada loop simétrico de dois nucleotídeos
em –2 Penaliza progressivamente loops simétricos com
mais de três nucleotídeos, assim como bulbos e loops assimétricos
Maximiza o tamanho de stem e minimiza o loop Um score total foi calculado pela fórmula:
(helical score +(ABS(G)/2))/2

Predição computacional de miRNA de Drosophila2. Identificar e avaliar qualidade de stem-loops
melhores 25.000 super-regiões Dm
regiões com maior score de cada super-
região
D. Melanogaster
(Dm)
D. Pseudoobscura
(Dp)
score médio de regiões pareadas
Dm/Dp
miRNA candidato -> regiões pareadas com maior score dentro de cada super-região
WU-BLAST de seq. Dm contra seq. de
Anopheles
score total dos melhores 3 hits, rankeados com o
score médio Dm/Dp
21/24 membros do conjunto referência Dm, foram agrupados com os melhores 600
candidatos a miRNA

Predição computacional de miRNA de Drosophila 3. Avaliar padrões de divergência em stem-loops conservados

Predição computacional de miRNA de Drosophila 3. Avaliar padrões de divergência em stem-loops conservados
Aplicação de Filtros booleanos – Remoção de regiões com alto score e/ou alta conservação que não são candidatas à miRNA. Trimagem da ponta fora do braço principal Blocos conservados de pelo menos 22 nt Estes blocos devem estar localizados a
aproximadamente 10 nucleotídeos do loop final Remoção das classes 4, 5 e 6 ~ 1/3 dos stem-loops conservados passaram pelos
filtros 18/24 (75%) sequências (conjunto referência)
estavam entre os primeiros 124 candidatos

Predição computacional de miRNA de Drosophila 3. Avaliar padrões de divergência em stem-loops conservados

Predição computacional de miRNA de Drosophila 3. Avaliar padrões de divergência em stem-loops conservados
570 passaram pelo filtro de conservação (barra verde) 124 miRseeker candidatos:
conjunto referência (verde) novos miRNA (azul) miRNA conservados em uma terceira espécie
(laranja)

Predição computacional de miRNA de Drosophila 3. Avaliar padrões de divergência em stem-loops conservados
Top 600 (21/24)
Após o filtro booleano: 200
(18/24)
42 novos candidatos em 200 melhores predições apresentaram conservação de sequência e estrutura em outras
espécies (Anopheles e Apis)

Validação experimental dos novos candidatos à miRNA
24 novos miRNA foram validados por northern-blot de RNA total isolado de embriões, larvas/pupa e adulto de Drosophila


Conclusão miRseeker identificou com sucesso os genes de miRNA
conhecidos em Drosophila 32 novos miRNA foram identificados pelo miRseeker, sendo
que 24 deles foram validados por northern blot estima-se a presença de 110 genes de miRNA em
Drosophila (1% dos genes codificantes, em concordância com vertebrados)
divergência dentro da região loop foi inesperada. Duas conclusões:
a região de loop parece ser menos crítica no pré-miRNA deve haver uma pressão de seleção na sequência que
forma a região stem, já que a Dicer atua na estrutura helicoidal (braço)

Referências bibliográficas Lai et al. (2003) Computacional identification of Drosophila microRNA genes. Genome Biology, 4(7):R42
Ambros (2001) MicroRNAs: Tiny regulators with Great Potential. Cell, 107: 823-826
Pasquinelli (2002) MicroRNAs: deviants no longer. TRENDS in Genetics 18(4):171-173
Moss (2002) MicroRNAs: Hidden in the Genome. Current Biology 12:R138-R140
Mount (2001) Bioinformatics. Sequence and Genome analysis. pp. 205-235
Bray et al.(2003) AVID: A Global Alignment Program. Genoma Research 13:97-102